Plotの描画関連
複数の時系列を縦に並べてplotする
ここに書いてある、gwpy.plotのPlot()がオススメ。
GUIで拡大等をしたとき、他のaxesも一緒に動く。
注意点は、TimeSeriesのlistやTimeSeriesDictを引数にしてまとめて渡した場合は separate=True をしても分割されないという謎仕様。面倒だが1つ1つ手で並べる必要がある。
戻り値 (ここでは plot)は、matplotlibのfigureだと思ってしまってよい。
なので、それぞれのy軸ラベルや全体のタイトルを付けるには以下のようにする。
時刻の基準を手で設定する
ここを参照
もしくはここ参照
DQ Flagを添える
.add_segments_bar() を使う(ここを参照)。
他にも .add_state_segments() や .add_dataqualityflag() といった似たものがある。詳細はPlotting APIを参照。
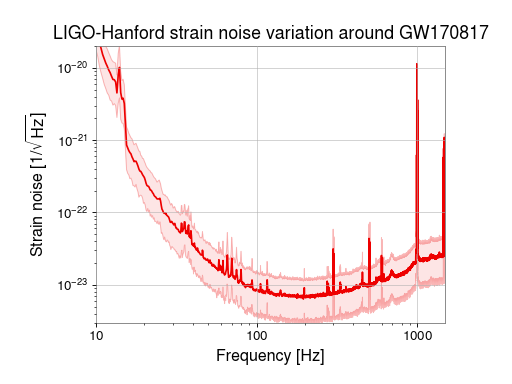
スペクトルのパーセンタイル/σバンドを付ける
ここを参照。手順としては、
まずTimeSeriesからspectrogram2()を使ってnon-averaged power Spectrogramを作る。
- .percentile() でパーセンタイルのスペクトルを3つ作る。
- plot_mmm() で描画するとバンド付きでplotされる。
1 from gwpy.timeseries import TimeSeries
2 from gwpy.plot import Plot
3
4 hoft = TimeSeries. ...
5 sg = hoft.spectrogram2(fftlength=4, overlap=2, window='hanning') ** (1/2.)
6 median = sg.percentile(50)
7 low = sg.percentile(5)
8 high = sg.percentile(95)
9
10 plot = Plot()
11 ax = plot.gca(xscale='log', xlim=(10, 1500), xlabel='Frequency [Hz]', yscale='log', ylim=(3e-24, 2e-20), ylabel=r'Strain noise [1/$\sqrt{\mathrm{Hz}}$]')
12 ax.plot_mmm(median, low, high, color='gwpy:ligo-hanford')
13 ax.set_title('LIGO-Hanford strain noise variation around GW170817', fontsize=16)
14 plot.show()
パーセンタイルではなくmeanとσで表したい場合は、Spectrogramの2次元配列に対して時間軸(0軸)方向にmean, stdを取ればよい。
matplotlib色々
imshow を使って2Dヒストグラムを書く時の軸の取り方
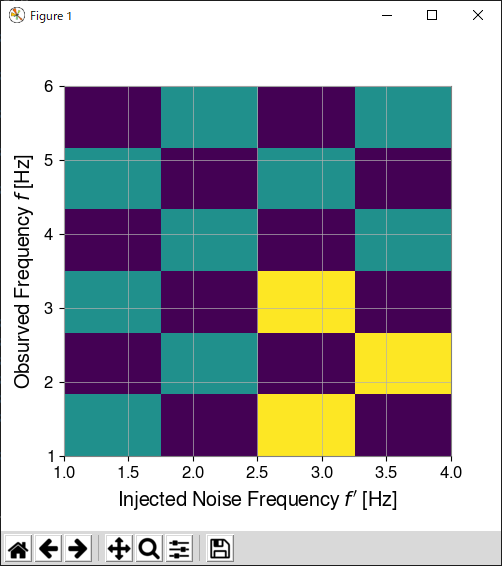
以下のような2変数f_in, f_outの間の相関データを、imshowを使って2Dヒストグラムとして描画したいとしよう。
素直に以下のように書くと、縦軸が反転して(上から下になる)しまい、bin幅もごみになる。
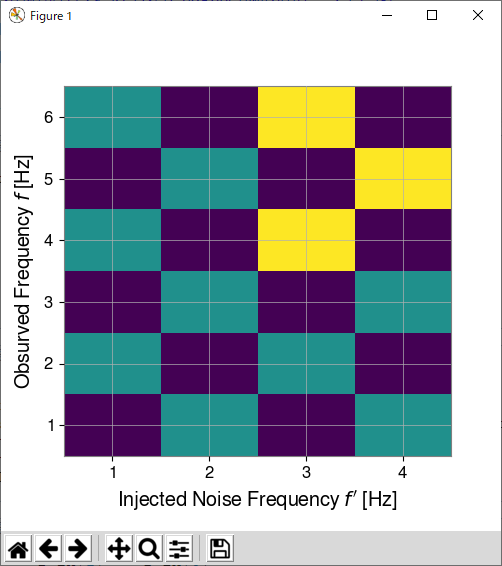
縦軸の向きは origin='lower' を入れると下から上になる。
bin幅については、上下左右に半分ずつ追加することで変数の値(今の場合はf_in, f_out)がbin中心になるようにできる。
1 df_in = f_in[1] - f_in[0]
2 df_out = f_out[1] - f_out[0]
3
4 f_L = f_in[0] - df_in*0.5
5 f_R = f_in[-1]+ df_in*0.5
6 f_B = f_out[0] - df_out*0.5
7 f_T = f_out[-1]+ df_out*0.5
8
9 fig = Plot(figsize=(5, 5))
10 ax = fig.gca()
11 ax.imshow(matrix, extent=[f_L, f_R, f_B, f_T], aspect='auto', origin='lower', interpolation='nearest')
12 ax.set_xlabel("Injected Noise Frequency $f'$ [Hz]")
13 ax.set_ylabel('Obsurved Frequency $f$ [Hz]')
14 fig.show()
TitleやLabelなどにアンダーバー(_)が含まれてると怒られる
環境によっては起きない問題だが、例えば神岡のK1sum*とかで発生する。
pythonやmatplotlibのバージョンの問題化と思いきや、virtualenvで最新環境にしても生じるので原因はよくわからない。
とりあえず、頭に以下のおまじないを付けると解決する。
正負両方の対数プロット